注意
转到末尾 下载完整的示例代码。或通过JupyterLite或Binder在浏览器中运行此示例
比较不同缩放器对包含异常值的数据的影响#
加利福尼亚住房数据集的特征0(街区中位数收入)和特征5(平均房屋入住率)具有非常不同的尺度,并且包含一些非常大的异常值。这两个特点导致难以可视化数据,更重要的是,它们会降低许多机器学习算法的预测性能。未缩放的数据也可能减慢甚至阻止许多基于梯度的估计器的收敛。
事实上,许多估计器是在假设每个特征取值接近零或更重要的是所有特征在可比尺度上变化的条件下设计的。特别是,基于度量和基于梯度的估计器通常假设近似标准化数据(具有单位方差的中心化特征)。一个显著的例外是基于决策树的估计器,它们对数据的任意缩放具有鲁棒性。
此示例使用不同的缩放器、转换器和归一化器将数据带入预定义的范围。
缩放器是线性(或更准确地说,仿射)转换器,它们在估计用于平移和缩放每个特征的参数的方式上彼此不同。
QuantileTransformer提供非线性变换,其中边缘异常值和异常点之间的距离被缩小。PowerTransformer提供非线性变换,其中数据被映射到正态分布以稳定方差并最小化偏度。
与之前的变换不同,归一化指的是每个样本的变换,而不是每个特征的变换。
以下代码有点冗长,您可以随意直接跳转到结果的分析。
# Authors: The scikit-learn developers
# SPDX-License-Identifier: BSD-3-Clause
import matplotlib as mpl
import numpy as np
from matplotlib import cm
from matplotlib import pyplot as plt
from sklearn.datasets import fetch_california_housing
from sklearn.preprocessing import (
MaxAbsScaler,
MinMaxScaler,
Normalizer,
PowerTransformer,
QuantileTransformer,
RobustScaler,
StandardScaler,
minmax_scale,
)
dataset = fetch_california_housing()
X_full, y_full = dataset.data, dataset.target
feature_names = dataset.feature_names
feature_mapping = {
"MedInc": "Median income in block",
"HouseAge": "Median house age in block",
"AveRooms": "Average number of rooms",
"AveBedrms": "Average number of bedrooms",
"Population": "Block population",
"AveOccup": "Average house occupancy",
"Latitude": "House block latitude",
"Longitude": "House block longitude",
}
# Take only 2 features to make visualization easier
# Feature MedInc has a long tail distribution.
# Feature AveOccup has a few but very large outliers.
features = ["MedInc", "AveOccup"]
features_idx = [feature_names.index(feature) for feature in features]
X = X_full[:, features_idx]
distributions = [
("Unscaled data", X),
("Data after standard scaling", StandardScaler().fit_transform(X)),
("Data after min-max scaling", MinMaxScaler().fit_transform(X)),
("Data after max-abs scaling", MaxAbsScaler().fit_transform(X)),
(
"Data after robust scaling",
RobustScaler(quantile_range=(25, 75)).fit_transform(X),
),
(
"Data after power transformation (Yeo-Johnson)",
PowerTransformer(method="yeo-johnson").fit_transform(X),
),
(
"Data after power transformation (Box-Cox)",
PowerTransformer(method="box-cox").fit_transform(X),
),
(
"Data after quantile transformation (uniform pdf)",
QuantileTransformer(
output_distribution="uniform", random_state=42
).fit_transform(X),
),
(
"Data after quantile transformation (gaussian pdf)",
QuantileTransformer(
output_distribution="normal", random_state=42
).fit_transform(X),
),
("Data after sample-wise L2 normalizing", Normalizer().fit_transform(X)),
]
# scale the output between 0 and 1 for the colorbar
y = minmax_scale(y_full)
# plasma does not exist in matplotlib < 1.5
cmap = getattr(cm, "plasma_r", cm.hot_r)
def create_axes(title, figsize=(16, 6)):
fig = plt.figure(figsize=figsize)
fig.suptitle(title)
# define the axis for the first plot
left, width = 0.1, 0.22
bottom, height = 0.1, 0.7
bottom_h = height + 0.15
left_h = left + width + 0.02
rect_scatter = [left, bottom, width, height]
rect_histx = [left, bottom_h, width, 0.1]
rect_histy = [left_h, bottom, 0.05, height]
ax_scatter = plt.axes(rect_scatter)
ax_histx = plt.axes(rect_histx)
ax_histy = plt.axes(rect_histy)
# define the axis for the zoomed-in plot
left = width + left + 0.2
left_h = left + width + 0.02
rect_scatter = [left, bottom, width, height]
rect_histx = [left, bottom_h, width, 0.1]
rect_histy = [left_h, bottom, 0.05, height]
ax_scatter_zoom = plt.axes(rect_scatter)
ax_histx_zoom = plt.axes(rect_histx)
ax_histy_zoom = plt.axes(rect_histy)
# define the axis for the colorbar
left, width = width + left + 0.13, 0.01
rect_colorbar = [left, bottom, width, height]
ax_colorbar = plt.axes(rect_colorbar)
return (
(ax_scatter, ax_histy, ax_histx),
(ax_scatter_zoom, ax_histy_zoom, ax_histx_zoom),
ax_colorbar,
)
def plot_distribution(axes, X, y, hist_nbins=50, title="", x0_label="", x1_label=""):
ax, hist_X1, hist_X0 = axes
ax.set_title(title)
ax.set_xlabel(x0_label)
ax.set_ylabel(x1_label)
# The scatter plot
colors = cmap(y)
ax.scatter(X[:, 0], X[:, 1], alpha=0.5, marker="o", s=5, lw=0, c=colors)
# Removing the top and the right spine for aesthetics
# make nice axis layout
ax.spines["top"].set_visible(False)
ax.spines["right"].set_visible(False)
ax.get_xaxis().tick_bottom()
ax.get_yaxis().tick_left()
ax.spines["left"].set_position(("outward", 10))
ax.spines["bottom"].set_position(("outward", 10))
# Histogram for axis X1 (feature 5)
hist_X1.set_ylim(ax.get_ylim())
hist_X1.hist(
X[:, 1], bins=hist_nbins, orientation="horizontal", color="grey", ec="grey"
)
hist_X1.axis("off")
# Histogram for axis X0 (feature 0)
hist_X0.set_xlim(ax.get_xlim())
hist_X0.hist(
X[:, 0], bins=hist_nbins, orientation="vertical", color="grey", ec="grey"
)
hist_X0.axis("off")
将为每个缩放器/归一化器/转换器显示两个图。左图将显示整个数据集的散点图,而右图将仅考虑99%的数据集(排除边缘异常值)来排除极值。此外,每个特征的边缘分布将显示在散点图的两侧。
def make_plot(item_idx):
title, X = distributions[item_idx]
ax_zoom_out, ax_zoom_in, ax_colorbar = create_axes(title)
axarr = (ax_zoom_out, ax_zoom_in)
plot_distribution(
axarr[0],
X,
y,
hist_nbins=200,
x0_label=feature_mapping[features[0]],
x1_label=feature_mapping[features[1]],
title="Full data",
)
# zoom-in
zoom_in_percentile_range = (0, 99)
cutoffs_X0 = np.percentile(X[:, 0], zoom_in_percentile_range)
cutoffs_X1 = np.percentile(X[:, 1], zoom_in_percentile_range)
non_outliers_mask = np.all(X > [cutoffs_X0[0], cutoffs_X1[0]], axis=1) & np.all(
X < [cutoffs_X0[1], cutoffs_X1[1]], axis=1
)
plot_distribution(
axarr[1],
X[non_outliers_mask],
y[non_outliers_mask],
hist_nbins=50,
x0_label=feature_mapping[features[0]],
x1_label=feature_mapping[features[1]],
title="Zoom-in",
)
norm = mpl.colors.Normalize(y_full.min(), y_full.max())
mpl.colorbar.ColorbarBase(
ax_colorbar,
cmap=cmap,
norm=norm,
orientation="vertical",
label="Color mapping for values of y",
)
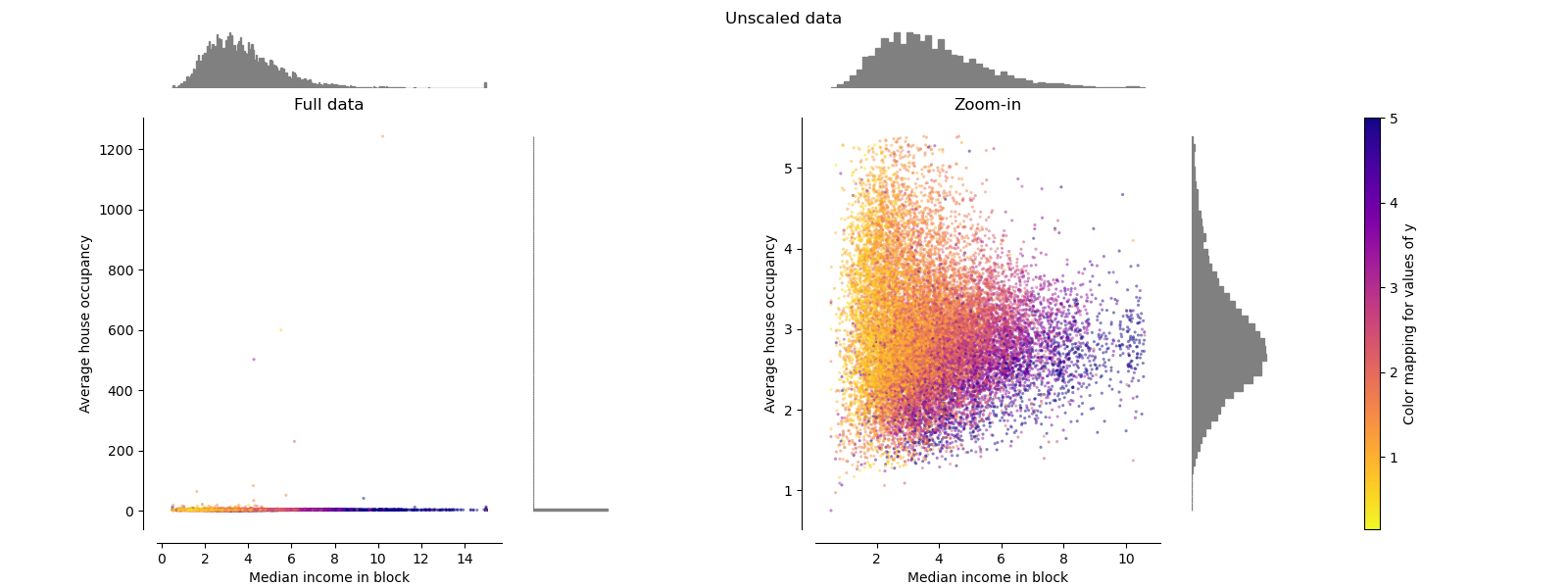
原始数据#
显示每个变换,显示两个转换后的特征,左图显示整个数据集,右图放大显示没有边缘异常值的数据集。大部分样本被压缩到特定范围,中位数收入为[0, 10],平均房屋入住率为[0, 6]。请注意,存在一些边缘异常值(某些街区的平均入住率超过1200)。因此,根据应用程序的不同,特定的预处理可能非常有益。在下文中,我们将介绍这些预处理方法在存在边缘异常值时的某些见解和行为。
make_plot(0)
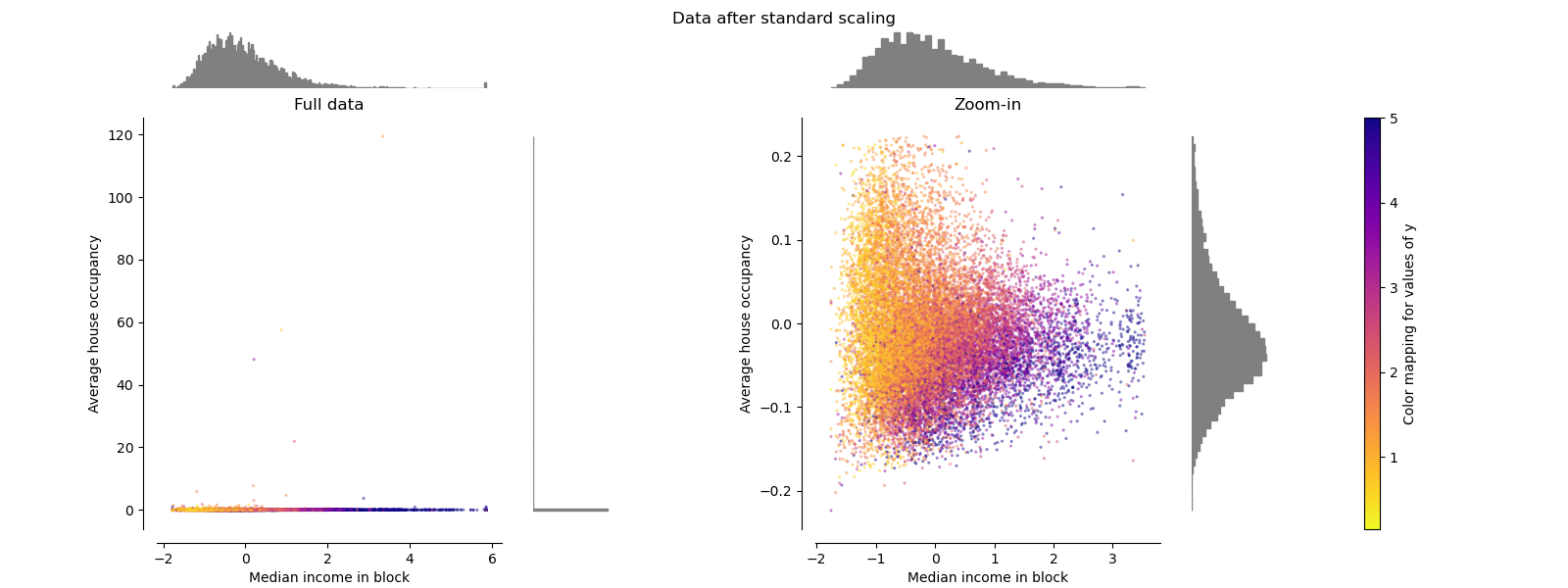
StandardScaler#
StandardScaler去除均值并将数据缩放为单位方差。如以下左图所示,缩放会缩小特征值的范围。但是,异常值在计算经验均值和标准差时会产生影响。尤其需要注意的是,由于每个特征上的异常值具有不同的幅度,因此每个特征上转换数据的分布差异很大:对于转换后的中位数收入特征,大部分数据位于[-2, 4]范围内,而相同的数据则被压缩到转换后的平均房屋入住率的较小范围[-0.2, 0.2]内。
StandardScaler因此不能保证在存在异常值的情况下特征尺度平衡。
make_plot(1)
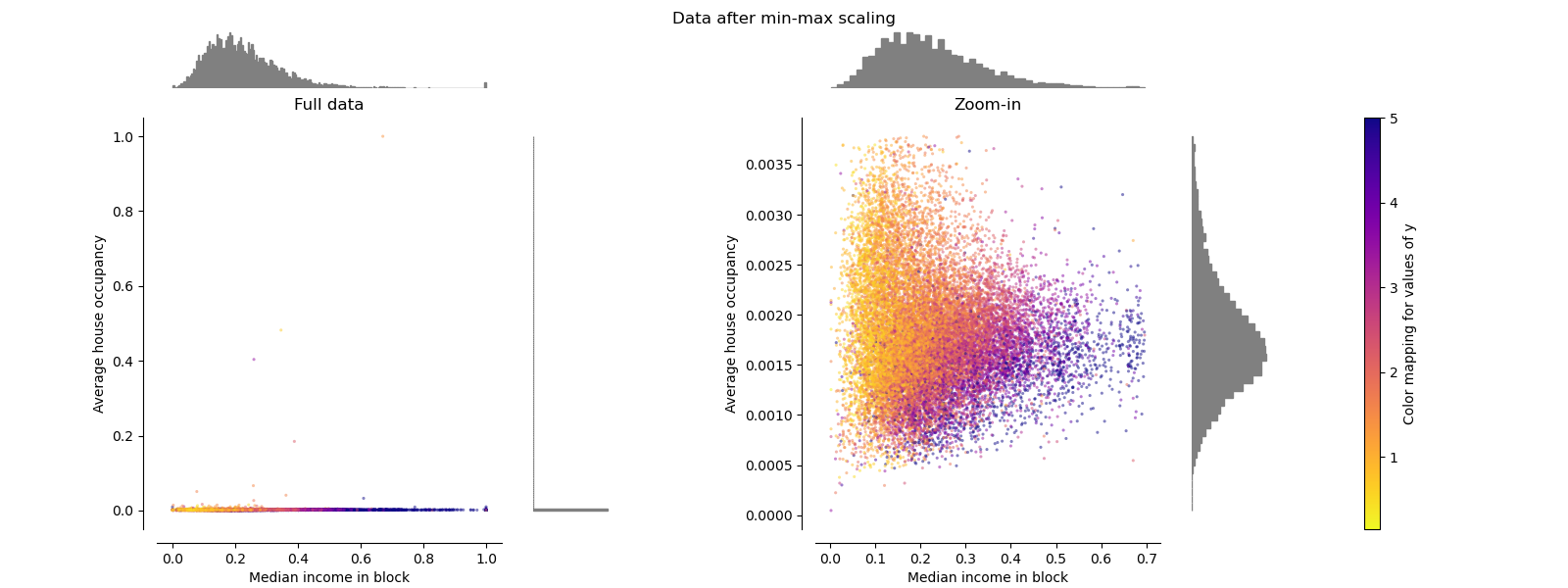
MinMaxScaler#
MinMaxScaler重新缩放数据集,使得所有特征值都在[0, 1]范围内,如下面的右图所示。但是,这种缩放会将所有异常点压缩到转换后的平均房屋入住率的狭窄范围[0, 0.005]内。
StandardScaler和MinMaxScaler都非常容易受到异常值的影响。
make_plot(2)
MaxAbsScaler#
MaxAbsScaler 与 MinMaxScaler 类似,但值的映射范围取决于是否存在负值或正值。如果只有正值,则范围为 [0, 1];如果只有负值,则范围为 [-1, 0];如果同时存在负值和正值,则范围为 [-1, 1]。在只有正值的数据上,MinMaxScaler 和 MaxAbsScaler 的行为相似。因此,MaxAbsScaler 也容易受到大型异常值的影响。
make_plot(3)
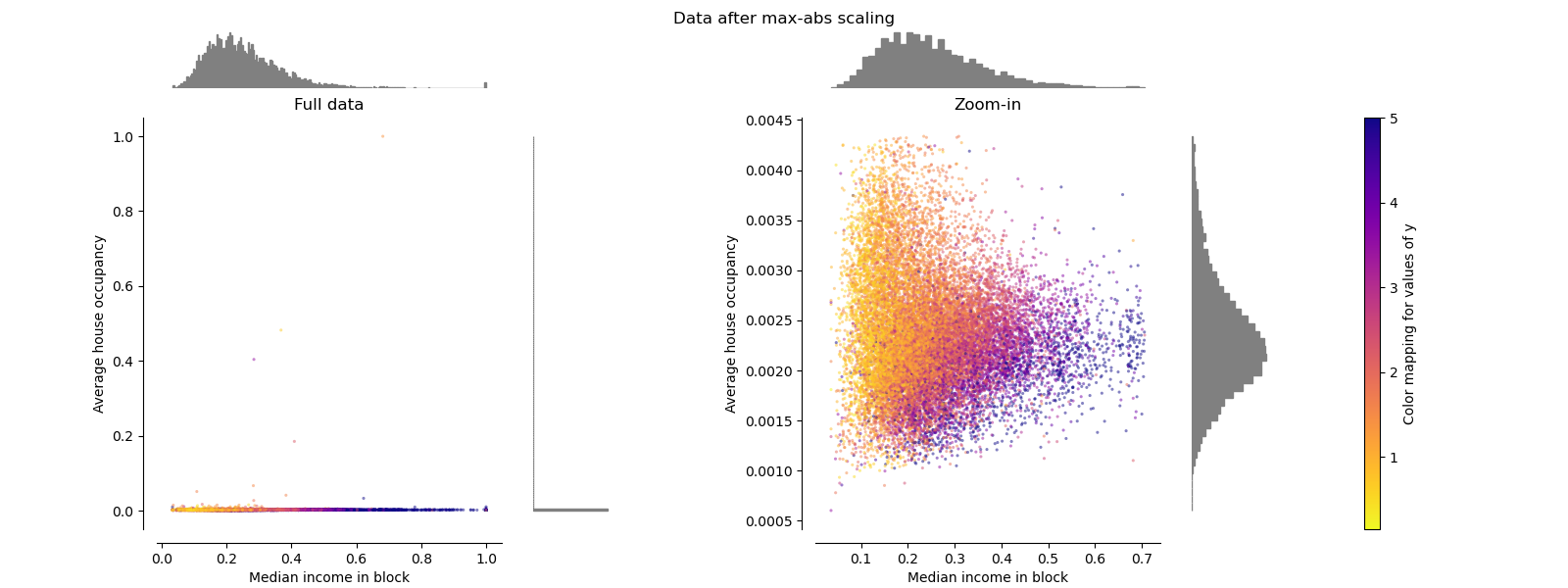
RobustScaler#
与之前的缩放器不同,RobustScaler 的居中和缩放统计数据基于百分位数,因此不受少量非常大的边缘异常值的影响。因此,变换后的特征值的范围比之前的缩放器更大,更重要的是,它们大致相似:对于这两个特征,大部分变换后的值都位于 [-2, 3] 范围内,如放大后的图中所示。请注意,异常值本身仍然存在于变换后的数据中。如果需要单独的异常值裁剪,则需要非线性变换(见下文)。
make_plot(4)
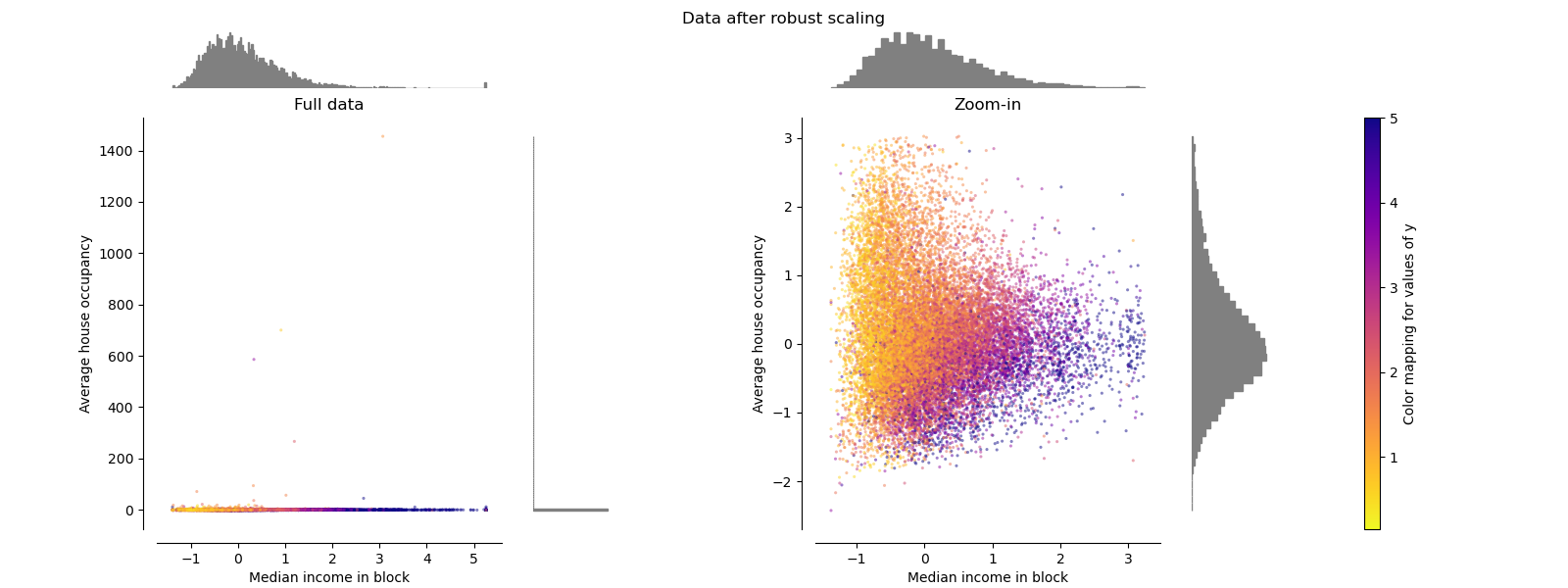
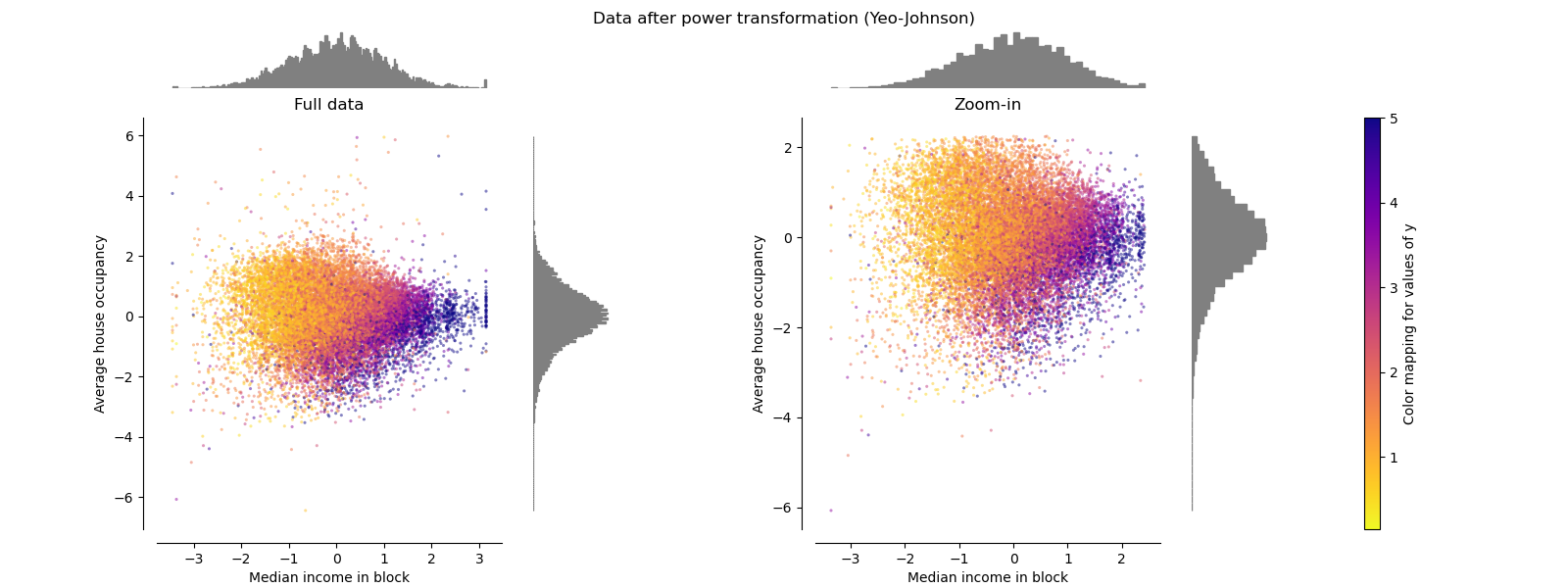
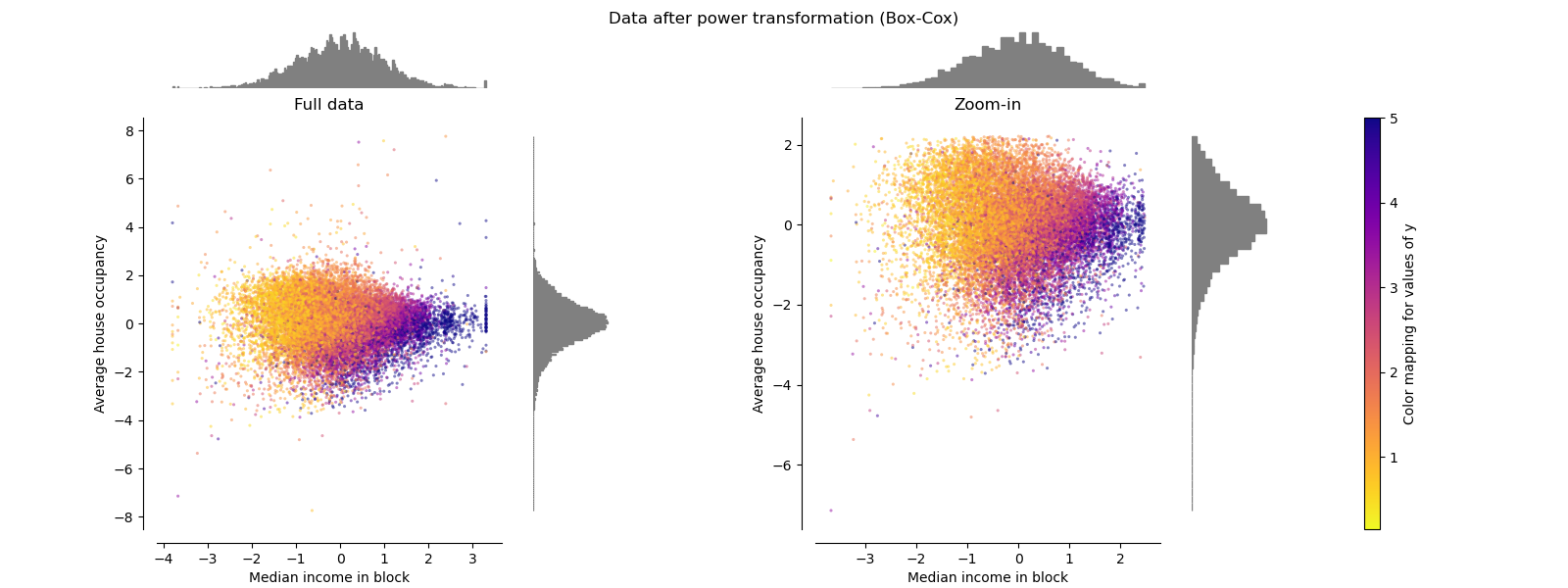
PowerTransformer#
PowerTransformer 对每个特征应用幂变换,使数据更接近高斯分布,以稳定方差并最小化偏度。目前支持 Yeo-Johnson 变换和 Box-Cox 变换,两种方法的最优缩放因子均通过最大似然估计确定。默认情况下,PowerTransformer 应用零均值、单位方差归一化。请注意,Box-Cox 变换只能应用于严格正值的数据。收入和平均房屋入住率恰好是严格正值,但如果存在负值,则优选 Yeo-Johnson 变换。
make_plot(5)
make_plot(6)
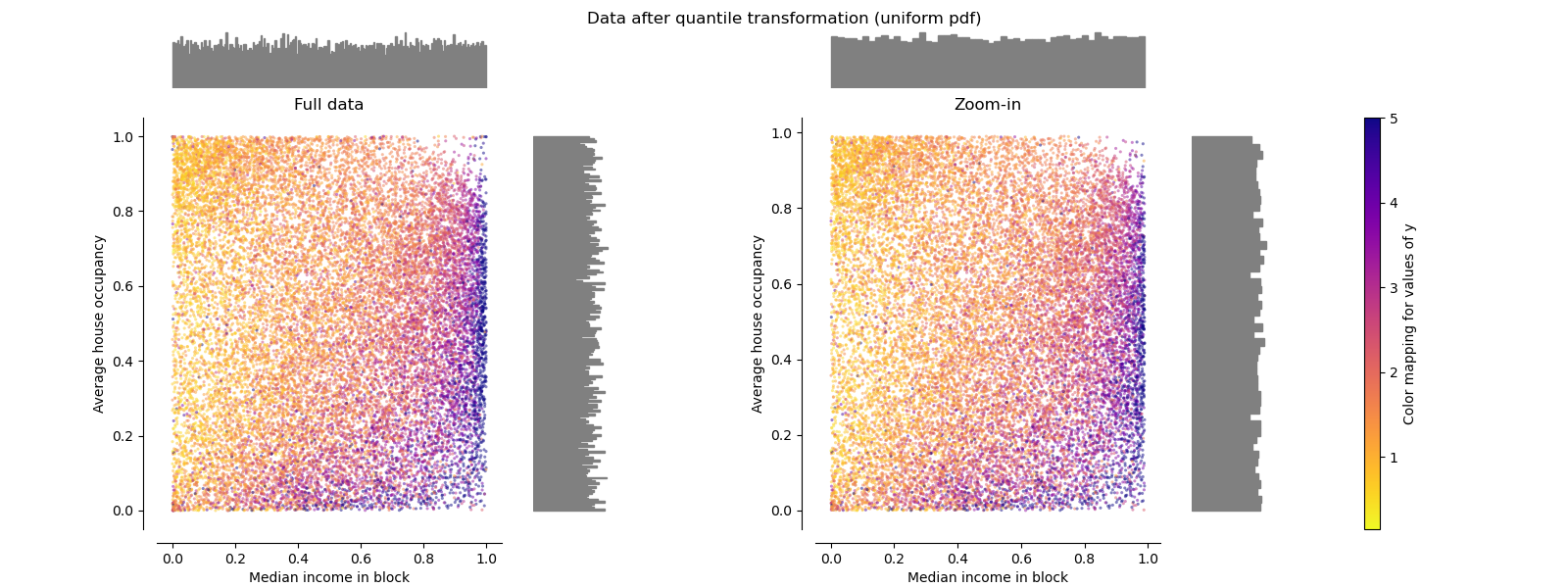
QuantileTransformer(均匀输出)#
QuantileTransformer 应用非线性变换,使得每个特征的概率密度函数将映射到均匀分布或高斯分布。在这种情况下,所有数据(包括异常值)都将映射到范围为 [0, 1] 的均匀分布,使异常值与内点无法区分。
RobustScaler 和 QuantileTransformer 对异常值具有鲁棒性,因为在训练集中添加或删除异常值将产生大致相同的变换。但与 RobustScaler 相反,QuantileTransformer 也会自动将任何异常值压缩到预先定义的范围边界(0 和 1)。这可能会导致极值出现饱和伪影。
make_plot(7)
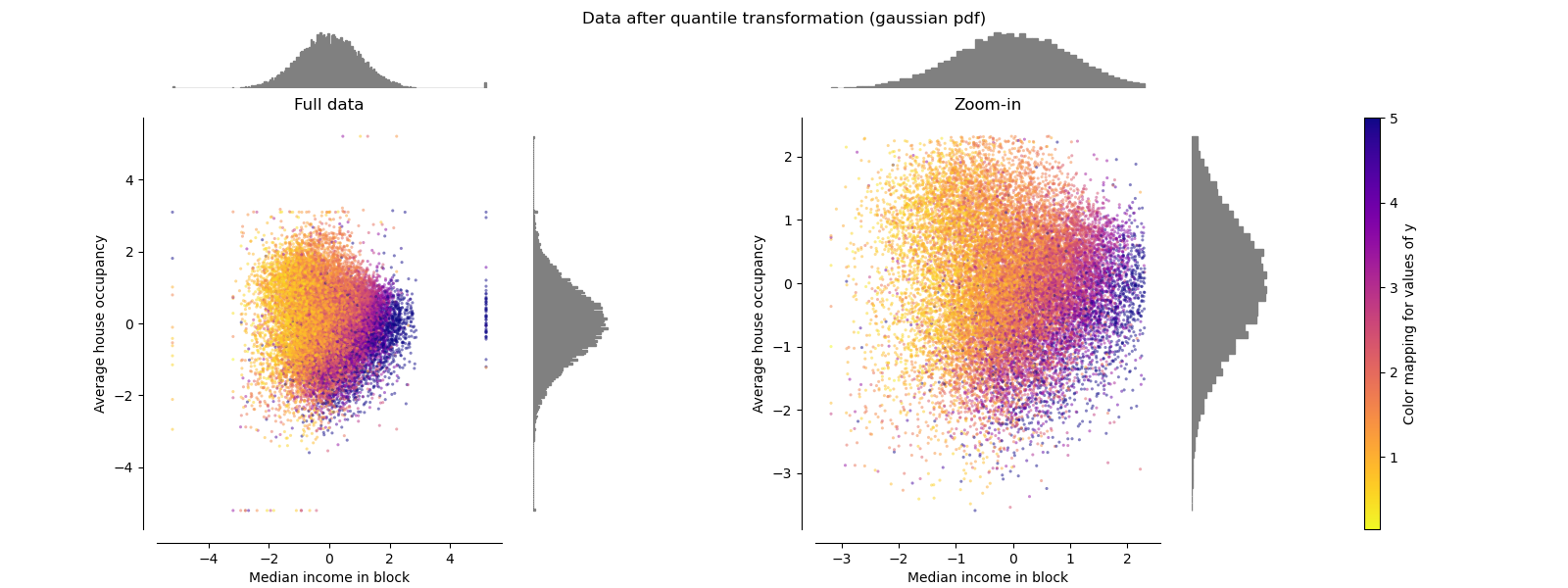
QuantileTransformer(高斯输出)#
要映射到高斯分布,请设置参数 output_distribution='normal'。
make_plot(8)
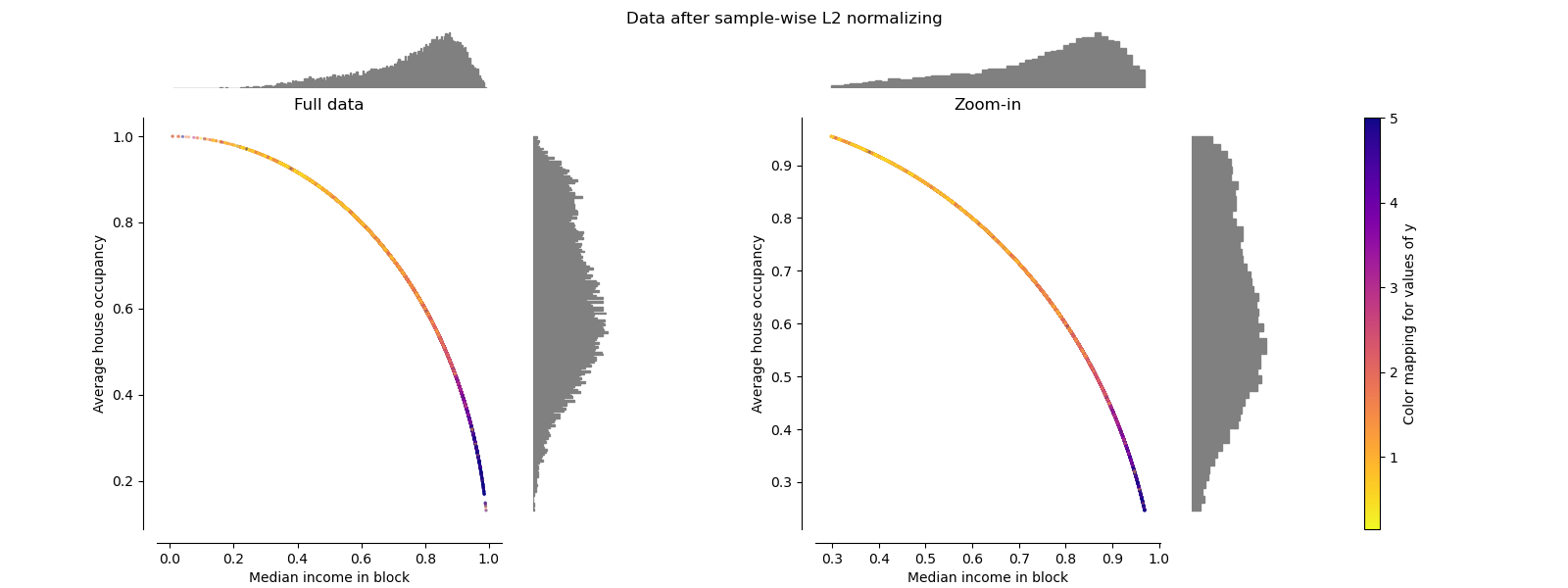
Normalizer#
Normalizer 将每个样本的向量重新缩放为单位范数,独立于样本的分布。这可以在下面的两个图中看到,所有样本都映射到单位圆上。在我们的例子中,选择的两个特征只有正值;因此,变换后的数据只位于正象限。如果一些原始特征混合了正值和负值,情况就不会是这样。
make_plot(9)
plt.show()
脚本总运行时间:(0 分钟 8.660 秒)
相关示例